文摘
人类微生物组的研究显示,即使是健康个体差异显著的微生物占据栖息地如肠道、皮肤和阴道。这种多样性仍然无法解释,虽然饮食、环境、主机遗传学和微生物接触都被牵连。因此,human-associated微生物群落的生态特征,人类微生物组计划分析了最大的群体和不同的临床相关的身体的栖息地。我们发现每个栖息地的多样性和丰富的签名微生物差异很大甚至在健康受试者中,具有较强的领域内部和之间的专业化的个人。项目遇到了估计有81 - 99%的属酶家庭和社区配置被西方健康的微生物。宏基因组代谢途径运输稳定个体尽管群落结构变化,和民族/种族背景被证明是最强大的关联路径和微生物与临床的元数据。这些结果因此划定的范围的微生物群落结构和功能配置正常健康的人口,使未来的描述流行病学、生态学和人类微生物组的转化应用。
主要
共有4788个标本242筛选和表型的成年人1(129,113)是可用在这项研究中,代表大多数的人类微生物组项目目标(HMP)的300人。成人疾病缺乏证据的受试者招募基于一份冗长的清单,列举排除标准;我们将把这里称为“健康”,作为定义的财团(k . Aagaard临床抽样标准et al。手稿提交)。妇女被采样18岁身体栖息地,男性在15个(不含三个阴道网站),分布在五个主要的身体区域。9从口腔及口咽标本收集:唾液;颊粘膜(脸颊)的,角质化的齿龈(牙龈),口感,扁桃体,喉咙和舌头软组织,超越和龈下的牙菌斑(牙牙龈之上和之下的生物膜)。四个皮肤标本收集两retroauricular折痕(每只耳朵后面)和两肘前的窝(内部肘部),和一个标本前鼻孔(鼻孔)。一个镇定的粪便标本代表降低胃肠道的微生物群,和三个阴道标本收集从阴道入口,中点和穹窿。评估受试微生物的稳定性,131人在这些数据在一个额外的取样时间点(平均219天,他第一次取样,后69天范围35 - 404天)。质量控制后,这些标本用于16 s rRNA基因分析通过454焦磷酸测序(缩写为今后16 s分析,指的是5408年和4605年他过滤序列/样本);681年评估函数,样本使用paired-end Illumina公司猎枪宏基因组测序读(平均2.9 Gb (Gb)和南达科他州。2.1 Gb /样本)1。提供了更多细节数据生成相关HMP出版物1而在补充的方法。
微生物多样性的人类健康
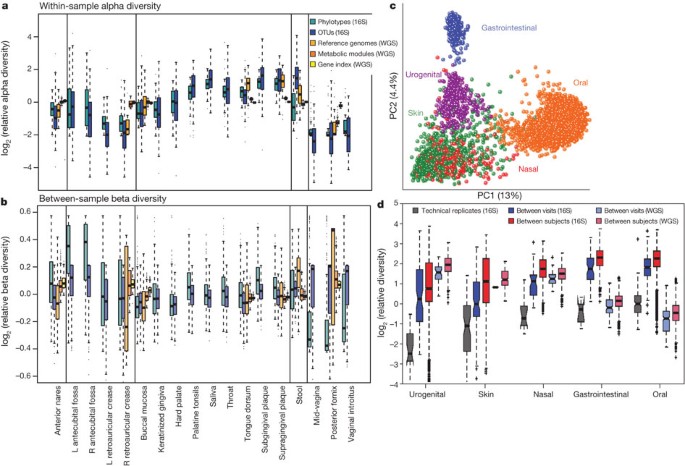
微生物在一个给定的身体栖息地的多样性可以定义为不同类型的生物的数量和数量分布,已与一些人类疾病:低多样性在肥胖和肠道炎症性肠病2,3例如,和高多样性阴道细菌性阴道炎4。对于这个大型研究涉及微生物样本收集的健康志愿者在美国的两个不同的地理位置,我们定义了每个身体的微生物群落栖息地,遇到81 - 99%的预测属饱和整体社区的范围配置(图1,补充图1和补充表1;参见图4)。口语和凳子社区尤其多样的社区成员,扩大前观察5,和阴道网站怀有特别简单的社区(图1一个)。本研究证实,这些模式的α多样性(样本)明显不同主体间对比样本相同的栖息地(β多样性,图1 b)。例如,唾液中最高的α多样性中值操作分类单元(辣子鸡,大约物种水平分类,看看http://hmpdacc.org/HMQCP),但最低的国家之一βdiversities-so虽然每个人的唾液是生态丰富,人口的成员共享类似的生物。相反,肘前的窝(皮肤)β多样性最高,但α多样性的中间。阴道α多样性最低,相当低的β多样性在属级但非常高的辣子鸡由于独特的存在乳酸菌spp。(图1 b)。群落结构变化的主要模式是身体的主要栖息地组(口腔、皮肤、肠道和阴道),定义结果全民主客体之间的完整的范围的变化人类微生物组的栖息地(图1 c)。受试的变化随着时间一直低于主客体之间变化,在有机合成和代谢功能(图1 d)。每个个体的独特性的微生物群落因此似乎稳定随时间(相对于人口作为一个整体),这可能是人类微生物组的另一个特点专门与健康有关。
一个由身体栖息地α多样性的主题,按地区分组,使用的相对逆辛普森指数衡量genus-level phylotypes(青色),16 s rRNA基因辣子鸡(蓝色),猎枪宏基因组读取匹配参考基因组(橙色),功能模块(暗橙色)和酶的家庭(黄色)。口通常显示高试多样性和阴道低多样性,与其他栖息地中间;个体之间的差异往往超过身体的栖息地之间的变化。b主体间,Bray-Curtisβ多样性通过身体栖息地,颜色的一个。皮肤最不同主题之间,用口服的栖息地和阴道属更稳定。虽然α-和beta-diversity不具有直接可比性,在社区结构的变化(一个)占据一个更广泛的动态范围比在社区个体之间的变化(b)。c,主坐标图显示样本之间的差异表明,主要的聚类是身体区域,口腔、胃肠道、皮肤和泌尿生殖栖息地分离;鼻孔栖息地桥梁口腔和皮肤的栖息地。d,重复样本相同的主题(蓝色)更类似微生物从不同主题(红色)。技术复制(灰色)反过来更相似;这些模式是一致的所有身体的栖息地和系统发育和代谢社区组成。看到先前描述的样本数量1所有的比较。
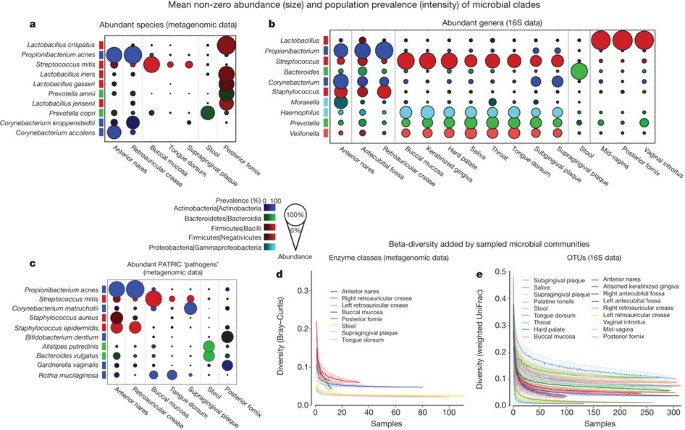
没有观察到类群是普遍存在在所有身体的栖息地和个人在使用的测序深度,与几个途径(图2和补充图2,见下文),尽管几个演化支了广泛流行和相对丰富的运输模式6,7。相反,正如单独提出的集中研究2,3,5,8,9身体,每个栖息地在几乎每一个主题是表现为一个或几个签名类群组成的多元化社区(图3)。签名在属级演化支形成平均17%到84%的各自身体的栖息地,完全没有在一些社区在这个级别的检测(0%)和代表整个人口(100%)。值得注意的是,更少的优势类群也高度个性化的,两个人之间和身体的栖息地;在口腔中,例如,大多数由栖息地链球菌,但这些都是富足的嗜血杆菌颊粘膜,放线菌supragingival斑块,普氏菌立即在相邻(但低氧)龈下的斑块10。
一个,b身体的栖息地,竖线代表微生物样品的七个地点猎枪和16 s数据;条指示微生物类群的相对含量,彩色的封存辣子鸡(一个)和代谢模块(b)。传说表明最丰富的类群/路径平均在一个或多个身体栖息地;RC, retroauricular折痕。多数的大多数社区的会员由一个占主导地位的门(通常属;看到补充图2),但这是普遍的所有身体的栖息地和所有人。相反,大部分代谢途径是均匀分布和流行的个人和身体的栖息地。
一个- - - - - -c患病率(强度、色彩表示门/类)和丰富的礼物(大小)的演化支健康的微生物。最丰富的metagenomically-identified物种(一个),16 s-identified属(b)和帕特里克12病原体(宏基因组)(c)所示。d,e,人口规模和测序深度的高分子聚合物有定义良好的微生物化验机构网站,所评估的饱和度增加社区代谢配置(稀疏最小Bray-Curtis beta-diversity近邻的宏基因组酶类丰度,内部四分位范围超过100个样本)(d)和系统配置(最小16 s OTU加权UniFrac距离最近的邻居)(e)。
提供了额外的分类详细的人类微生物组通过识别独特的标记序列在宏基因组数据11(图3)来补充16 s分析(图3 b)。这两个配置文件通常是密切协议(补充图3),前者在某些情况下提供更具体的信息签名成员属不同生境(例如,阴道内普氏菌amnii和肠道普氏菌copri)或个体(例如,阴道乳酸菌spp。)这方面的一个应用特异性确认没有NIAID(国家过敏症和传染病研究所)a - c类病原体丰富(除了0.1%以上金黄色葡萄球菌和大肠杆菌)健康的微生物,但投机取巧的近乎普及和广泛分布的病原体所定义的帕特里克12。规范的病原体包括霍乱弧菌,鸟型分支杆菌,空肠弯曲杆菌和沙门氏菌血清没有检测到这种程度的敏感性。幽门螺杆菌在只有两个粪便样本,被发现在< 0.01%,大肠杆菌出席丰度> 0.1% 15%的粪便微生物丰度在61% (> 0%)。对于一小部分也获得了类似的了解观察粪便样本有454焦磷酸测序用PhylOTU宏基因组数据13,14。327年总共56帕特里克病原体检测健康的微生物(> 1%患病率丰度> 0.1%,补充表2),所有机会,引人注目的是,通常普遍都在主机和栖息地。后者是与许多最丰富的类群签名,通常是更habitat-specific和主机之间的变量(图3 a, b)。这整体缺乏特别有害的微生物支持假设即使这个群体的多样性高,配置的微生物群往往占据了一系列健康不同于许多疾病扰动研究迄今为止3,15。
马车的特定微生物
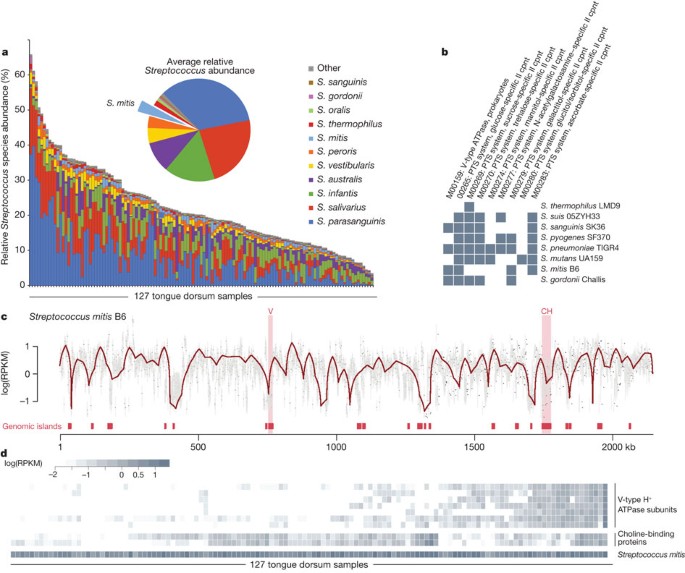
Inter-individual微生物被证明特定的变化,相关功能和个性化。这方面的一个例子所示链球菌种虫害的口腔。属支配着口咽16身体,不同物种丰富的在每个采样(见栖息地http://hmpdacc.org/HMSMCP),即使在物种水平,标志着马车在每个栖息地的个体差异(图4)。锅的比率——在许多human-associated core-genomes高微生物17,这丰富的变化可能是由于选择性压力作用于通路中不同的礼物链球菌物种或品种(图4 b)。事实上,我们观察到大量strain-level基因变异在微生物物种在这个人口,丰富的寄主专一性的结构变异在基因组岛(图4摄氏度)。甚至对单一链球菌应变B6,基因损失与这些事件很常见,例如不同的消除美国缓和的马车的v形atp酶或胆碱结合蛋白cbp6和cbp12子集的主机数量(图4 d)。这些损失很容易观察到的参考基因组分离相比,和这些初步结果表明,微生物菌株,收益和寄主专一性的基因多态性可能是同样无处不在。
宏基因组读取从127年跨越90例舌样本处理MetaPhlAn确定每个物种的相对含量。一个,11个不同的相对丰度链球菌spp。除了在更广泛的演化支变异(见图2),个别物种在一个栖息地演示各种成分变化。插图显示了平均舌样本的组成。b,代谢模块/ KEGG缺席(灰色/白色)24参考基因组的舌头链球菌表示选定地区的毒株特异性功能分化。cpnt,组件。c、比较基因组覆盖率为单身链球菌B6株。灰色点平均每千碱基读取每百万读取(RPKM)为1 kb windows,灰色酒吧是第75百分位数的25日在所有样本,红线LOWESS-smoothed平均水平。红条底部突出预测基因组岛27。大、离散和高度可变的岛屿通常未被充分代表。d,两个岛引人注目,V (V形H+atp酶亚基I、K、E、C、F, A和B)和CH (choline-binding蛋白质cbp6 cbp12),指示功能内聚性毒株特异性基因的个体人类宿主内损失。
功能相关的其他例子inter-individual变异的物种和应变发生在整个微生物水平。在肠道,脆弱拟杆菌可以' t细胞反应通过荚膜多糖在动物模型18这个分类单元,HMP粪便样本进行至少0.1%的水平在16%的样品(3%)超过1%的丰度。叫多形拟杆菌研究了对宿主胃肠道代谢的影响呢19同样常见的患病率46%。在皮肤上,金黄色葡萄球菌耐甲氧西林的,特别感兴趣的原因金黄色葡萄球菌(MRSA)感染,皮肤马车利率鼻了29%和4%,与预期基本相符20.。关闭系统发育等亲戚葡萄球菌epidermidis(自己认为共生体),相比之下,普遍在皮肤上,出现在93%的鼻孔样本,和在另一个极端铜绿假单胞菌(革兰氏阴性代表皮肤病原体)完全缺席身体栖息地在这种级别的检测(0%)。以上数据表明,一些物种在人类微生物组的运输模式可能类似于遗传性状,隐性等位基因的适度的风险保持在一个人口。在人类微生物组的情况下,高风险病原体依然缺席,而物种构成适度风险程度似乎也稳定保持在这个生态位。
最后,和体内微生物栖息地展出关系暗示驱动物理因素,如氧气、水分和pH值、宿主免疫因素,微生物的相互作用,如共生或竞争21(补充图4)。整体社区相似度和微生物共生和co-exclusion人类微生物组分组18身体栖息地一起到四个集群对应五个目标身体区域(补充图4 a, b)。阴道几乎没有区别在不同的网站乳酸菌种虫害控制所有三个,在大量相关。然而,乳酸菌不同的反向放线菌和拟杆菌(见补充图4 c和无花果2和3),也观察到前一个队列9。肠道微生物群的关系主要是由逆关联的拟杆菌占主导地位,包括在一些学科中少数人进行更大的壁厚菌门的多样性。皮肤明显出现了类似的发展社区,由之一葡萄球菌(门壁厚菌门),丙酸菌属,或棒状杆菌属(包括门放线菌),连续的口服生物(例如,链球菌)出现在鼻孔社区(补充图4 c)。这些观察结果表明,微生物群落结构在这些人有时可能会占据离散配置和在其他情况下不断变化,主题详细论述了HMP调查(ref。6和未发表的结果)。个人的位置在这样配置说明目前微生物运输(包括病原体)和社区的未来抵抗病原体的能力收购或失调;它可能因此被证明是与疾病易感性或其他相关表型特征。
微生物代谢和功能
作为第一个研究跨身体栖息地包括标志基因和宏基因组数据从一个大的人口,我们另外评估微生物代谢和功能的生态途径在这些社区。我们重建路径的相对丰度在社区基因组22,多比是常数和均匀多样化生物的丰度(图2 b,看到也图1),确认这是一个生态整个人类微生物组的属性2。我们同样能够确定首次跨微生物群落分类和功能α多样性显著关联(逆辛普森的枪兵r= 0.60,P= 3.6×10−67,n= 661),后者更被禁的社区范围内配置(补充图5)。
与微生物类群,不同个体之间的几个途径被无处不在的和身体的栖息地。这些“核心”的最丰富的途径包括核糖体和转化机械、核苷酸充电和ATP合成、糖酵解,反映host-associated微生物的基础知识。也与类群相比,一些通路中高度可变对象在任何身体的栖息地;异常包括Sec(口头,南达科他州途径相对丰富。= 0.0052;总意味着南达科他州的口头标准差= 0.0011。= 0.0016)和乙(在全球范围内,南达科他州途径。= 0.0055;南达科他州意味着全球标准差= 0.0023 = 0.0033)分泌系统,显示高度的宿主和microbe-microbe健康人类微生物群的交互。这么高的变化尤其存在于口腔;磷酸,mono di-saccharide,粘膜和氨基酸运输;和脂多糖生物合成和亚精胺/斑块和舌头上的腐胺的合成和运输(http://hmpdacc.org/HMMRC)。这个管家的稳定性和高基因变体丰富的“核心”与niche-specific功能更大的可变性和低丰度的罕见但始终存在通路;例如,亚精胺生物合成蛋氨酸退化和硫化氢生产,所有的例子在胃肠道的身体高度流行网站(非零> 92%的样本),但在非常低丰度(平均相对丰度< 0.0052)。这种“长尾”的low-abundance基因和通路也可能编码无特征的生物分子功能和新陈代谢的基因组,它的表达水平在未来的metatranscriptomic研究仍有待探讨。
蛋白质家庭显示多样性和流行趋势类似于完整的路径,从最大值∼16000独特的家庭/社区在阴道近400000在口腔(图1 a, b;http://hmpdacc.org/HMGI)。这些家庭的分数确实是功能无特征,包括那些被读取映射,最小的口腔南达科他州(平均58%。6.8%)和最大的鼻孔南达科他州(平均77%。11%)。同样,许多基因注释的程序集不能被分配一个代谢功能,通过最小阴道南达科他州(平均78%。3.4%)和最大肠道(意味着其中86%。0.9%)。后者由身体的栖息地范围没有明显差异,密切与先前的全面协议基因肠道metagenome的目录3。结合上面的微生物变化观察到整个人类微生物组,功能变异个体可能表示特别重要的途径在维持群落结构面对个性化的免疫,环境或膳食暴露在这些科目。确定函数变量的蛋白质和无特征的核心家庭尤其必要理解健康和疾病的微生物群的作用。
与东道国表型相关性
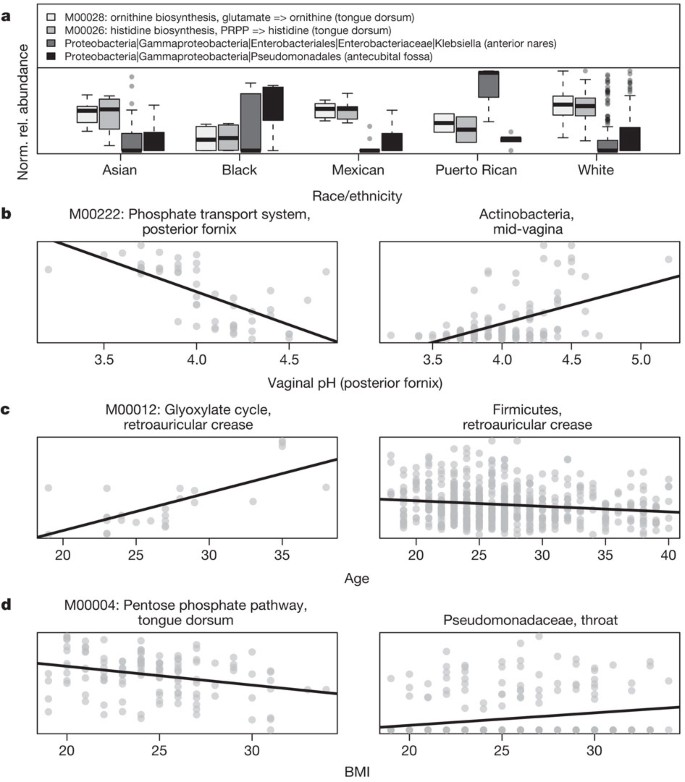
我们终于检查关系将演化支和代谢的微生物群与主机属性,比如年龄、性别、体重指数(BMI)和其他临床可用元数据(图5和补充表3)。使用稀疏的多变量模型,960年微生物、酶或通路丰度显著相关的一个或多个15主题表型和样本的元数据特性。各种各样的类群,基因家族和代谢途径与主体民族在每一个不同的分布式身体栖息地(图5),代表数量最多的表现型(266错误发现率(罗斯福)问总协会与微生物的< 0.2)。阴道的pH值也被观察到与微生物组成9,我们发现在这个人口预期的减少乳酸菌在高pH值和相应增加代谢多样性(图5 b)。有趣的是,而不是先前观察到的,年龄是最相关的一组高度差metagenomically编码路径在皮肤上(图5度),以及皮肤的变化演化支包括retroauricular厚壁菌门(P= 1.0×10−4,问= 0.033)。对种族和阴道的pH值的例子是最强的协会与微生物之一,然而,大多数相关(例如,使用BMI,图5 d)更典型地谦虚。这种低程度的相关性对于大多数可用的生物识别技术(性别、温度、血压等),连最重要的协会拥有一般低尺度效应和可观的无法解释的方差。我们得出结论,人类的大多数变异微生物并不是解释这些表型的元数据,和其他潜在的重要因素,如短期和长期的饮食,每日周期,创始人的影响如分娩方式,和宿主基因应该考虑在未来的分析。
一个- - - - - -d相关的途径和最重要的进化枝丰度(罗斯福问< 0.2)使用与主题种族多元线性模型(一个)、阴道后穹窿的pH值(b),年龄(c)和BMI (d)。散点图的样本所示用线条表示最简单的线性。种族/民族和阴道的pH值是特别强关联;年龄和体重指数更代表通常温和的表型关联(补充表3),这表明健康的细菌的差异可能与其他主机或环境因素相对应。
结论
这广泛的抽样的人类微生物组在许多学科和身体栖息地提供了健康成年人的正常微生物群的初始特征在西方人口。许多网站的大样本大小和一致的抽样从同一个人首次允许微生物之间的关系的理解,和微生物与临床参数,支撑的基础个体variation-variation可能最终理解microbiome-based疾病至关重要。临床研究的微生物能够利用由此产生的广泛的目录分类单元,途径和基因1,尽管他们还必须包括仔细匹配的内部控制。每个人的独特性的微生物甚至在这个参考人口认为未来的研究要考虑潜在的受试设计。高分子聚合物的独特组合在身体器官和功能数据的栖息地,包括16 s和宏基因组分析,结合每个主题的详细描述,使我们和后续研究超越变化的观察人类微生物组问如何以及为什么这些微生物群落变化如此广泛。
许多细节仍进一步填写工作,建立在该参考研究。如何早期殖民和一生的改变在身体不同的栖息地?流行病学的传播模式有益或无害的微生物镜像病原体的传播模式?之间的共生微生物反映共同应对环境问题,而不是竞争或互惠互动?多大宿主免疫力或基因发挥作用在塑造模式的多样性,以及观察到的模式如何在这个北美人口与周围的世界?未来的研究基础上建立的基因和生物目录人类微生物组项目,包括metatranscriptomes日益详尽的调查和metaproteomes,将有助于解开这些开放的问题,让我们更全面地理解人类微生物组之间的联系,健康和疾病。
方法总结
微生物样本收集从18身体网站在一个或两个时间点从242个人临床缺乏疾病(k . Aagaard筛查et al。手稿提交)。样品受到16 s核糖体RNA基因焦磷酸测序(454生命科学),和一个子集shotgun-sequenced使用Illumina公司为宏基因组GAIIx平台1。16 s数据处理和使用QIIME多样性进行了估计23使用MetaPhlAn,宏基因组数据分类学的异形11,由HUMAnN新陈代谢异形22和组装的基因注释和集群独特的目录1。潜在的病原体被确定使用帕特里克数据库12、隔离来自KEGG参考基因组注释24和参考基因组由BWA映射25减少组的基因组短读可以匹配26。微生物协会是占组合的相似性评估措施21和表型关联测试是在r .执行所有数据和附加协议可查看详情http://hmpdacc.org。全陪本文的方法补充信息。
引用
人类微生物组项目财团。人类微生物组研究的框架。自然http://dx.doi.org/10.1038/nature11209(这个问题)
恩伯,p . j . et al .核心肠道微生物在肥胖和精益双胞胎。自然457年480 - 484 (2009)
秦,j . et al。人类肠道微生物基因目录建立了宏基因组测序。自然464年59 - 65 (2010)
弗雷德里克·d . N。,Fiedler, T. L. & Marrazzo, J. M. Molecular identification of bacteria associated with bacterial vaginosis.心血管病。j .地中海。353年1899 - 1911 (2005)
Costello, e . k . et al .细菌社区人体栖息地的变化在时间和空间。科学326年1694 - 1697 (2009)
休斯,S。,你们,Y。,Zhou, Y. & Fodor, A. A core human microbiome as viewed through 16s rRNA sequences clusters.《公共科学图书馆•综合》http://dx.doi.org/10.1371/journal.pone.0034242(2012年6月14日)
李,K。,Bihan, M., Yooseph, S. & Methe, B. A. Analyses of the microbial diversity across the human microbiome.《公共科学图书馆•综合》http://dx.doi.org/10.1371/journal.pone.0032118(2012年6月14日)
格赖斯、e·a . et al .地形和世俗的人类皮肤微生物的多样性。科学324年1190 - 1192 (2009)
拉威尔,j . et al .生育年龄女性的阴道微生物。Proc。《科学。美国108年(1)4680 - 4687 (2011)
Segata: et al。成人消化道微生物组成基于七口表面、扁桃体、喉咙和粪便样本。基因组医学杂志。13R42 (2012)
Segata: et al。有效的宏基因组微生物群落分析使用独特clade-specific标记基因。自然方法http://dx.doi.org/10.1038/nmeth.2066(2012)
Gillespie, j。j。帕特里克:全面关注人类致病性细菌生物信息学资源物种。感染。Immun。79年4286 - 4298 (2011)
夏普顿t . j . et al . PhylOTU:高通量过程量化微生物群落多样性和解析小说分类单元从宏基因组数据。公共科学图书馆第一版。医学杂志。7e1001061 (2011)
威利,k . m . et al .小说人类微生物组的细菌类群。《公共科学图书馆•综合》http://dx.doi.org/10.1371/journal.pone.003529(2012年6月14日)
索科尔,h . et al。Faecalibacterium prausnitzii是一种抗炎共生的细菌被肠道微生物群的分析克罗恩病的病人。Proc。《科学。美国105年16731 - 16736 (2008)
原子吸收光谱法,j . A。,P一个ster, B. J., Stokes, L. N., Olsen, I. & Dewhirst, F. E. Defining the normal bacterial flora of the oral cavity.j .中国。Microbiol。435721 - 5732 (2005)
Medini, d . et al .微生物学后基因时代。启Microbiol性质。6419 - 430 (2008)
Mazmanian美国K。,Round, J. L. & Kasper, D. L. A microbial symbiosis factor prevents intestinal inflammatory disease.自然453年620 - 625 (2008)
古德曼,a . l . et al。确定遗传因素需要建立一个人类肠道共生有机体在其栖息地。细胞宿主细菌6279 - 289 (2009)
Kuehnert, m . j . et al .患病率金黄色葡萄球菌鼻殖民在美国,2001 - 2002。j .感染。说。193年172 - 179 (2006)
浮士德,k . et al .微生物共生关系在人类微生物组。公共科学图书馆第一版。医学杂志。(媒体)
Abubucker, s . et al .代谢重建人类微生物宏基因组数据及其应用。公共科学图书馆第一版。医学杂志。http://dx.doi.org/10.1371/journal.pcbi.1002358(2012年6月14日)
Caporaso, j·g . et al . QIIME允许社区高通量测序数据的分析。自然方法7335 - 336 (2010)
Kanehisa, M。Goto, S。,Furumichi, M., Tanabe, M. & Hirakawa, M. KEGG for representation and analysis of molecular networks involving diseases and drugs.核酸Res。38D355-D360 (2010)
李,h &杜宾,r .快速和准确的读与burrows - wheeler变换。生物信息学26589 - 595 (2010)
Giannoukos, g . et al .高效和健壮RNA-seq过程培养细菌转录组和复杂的社区。基因组医学杂志。13R23 (2012)
Langille, m . g . & Brinkman, f·s·IslandViewer:一个集成的计算识别和可视化界面的基因组岛。生物信息学25664 - 665 (2009)
确认
该财团要感谢我们的外部科学顾问委员会:r·布隆伯格j·戴维斯,r·霍尔特·Ossorio Ouellette), g . Schoolnik和a·威廉森。我们还要感谢我们的合作者在国际人类微生物组的财团,特别是MetaHIT项目的调查,为推进人类微生物组研究。提供的数据存储库管理是国家生物技术信息中心和美国国立卫生研究院的校内研究项目国家医学图书馆。我们欣赏个人的参与从圣路易斯,密苏里州和得克萨斯州休斯敦的地区使这项研究成为可能。这项研究是由美国国立卫生研究院的资助支持部分U54HG004969 B.W.B.;U54HG003273 R.A.G.;U54HG004973, R.A.G.,S.K.H. J.F.P.;U54HG003067 E.S.Lander;U54AI084844 K.E.N.;N01AI30071 R.L.Strausberg; U54HG004968 to G.M.W.; U01HG004866 to O.R.W.; U54HG003079 to R.K.W.; R01HG005969 to C.H.; R01HG004872 to R.K.; R01HG004885 to M.P.; R01HG005975 to P.D.S.; R01HG004908 to Y.Y.; R01HG004900 to M.K.Cho and P. Sankar; R01HG005171 to D.E.H.; R01HG004853 to A.L.M.; R01HG004856 to R.R.; R01HG004877 to R.R.S. and R.F.; R01HG005172 to P. Spicer.; R01HG004857 to M.P.; R01HG004906 to T.M.S.; R21HG005811 to E.A.V.; M.J.B. was supported by UH2AR057506; G.A.B. was supported by UH2AI083263 and UH3AI083263 (G.A.B., C. N. Cornelissen, L. K. Eaves and J. F. Strauss); S.M.H. was supported by UH3DK083993 (V. B. Young, E. B. Chang, F. Meyer, T. M. S., M. L. Sogin, J. M. Tiedje); K.P.R. was supported by UH2DK083990 (J. V.); J.A.S. and H.H.K. were supported by UH2AR057504 and UH3AR057504 (J.A.S.); DP2OD001500 to K.M.A.; N01HG62088 to the Coriell Institute for Medical Research; U01DE016937 to F.E.D.; S.K.H. was supported by RC1DE0202098 and R01DE021574 (S.K.H. and H. Li); J.I. was supported by R21CA139193 (J.I. and D. S. Michaud); K.P.L. was supported by P30DE020751 (D. J. Smith); Army Research Office grant W911NF-11-1-0473 to C.H.; National Science Foundation grants NSF DBI-1053486 to C.H. and NSF IIS-0812111 to M.P.; The Office of Science of the US Department of Energy under Contract No. DE-AC02-05CH11231 for P.S. C.; LANL Laboratory-Directed Research and Development grant 20100034DR and the US Defense Threat Reduction Agency grants B104153I and B084531I to P.S.C.; Research Foundation - Flanders (FWO) grant to K.F. and J.Raes; R.K. is an HHMI Early Career Scientist; Gordon & Betty Moore Foundation funding and institutional funding from the J. David Gladstone Institutes to K.S.P.; A.M.S. was supported by fellowships provided by the Rackham Graduate School and the NIH Molecular Mechanisms in Microbial Pathogenesis Training Grant T32AI007528; a Crohn’s and Colitis Foundation of Canada Grant in Aid of Research to E.A.V.; 2010 IBM Faculty Award to K.C.W.; analysis of the HMP data was performed using National Energy Research Scientific Computing resources, the BluBioU Computational Resource at Rice University.
作者信息
作者和联系
财团
贡献
主要调查人员:B.W.B.,R.A.G.,S.K.H.,B.A.M.,K.E.N.,J.F.P.,G.M.W.,O.W.,上面W. Manuscript preparation: D.G., C.H., R.K., O.W. Funding agency management: C.C.B., T.B., V.R.B., J.L.C., S.C., C.D., V.D.F., C.G., M.Y.G., R.D.L., J.M., P.M., J.P., L.M.P., J.A.S., L.W., C.W., K.A.W. Project leadership: S.A., J.H.B., B.W.B., A.T.C., H.H.C., A.M.E., M.G.F., R.S.F., D.G., M.G.G., K.H., S.K.H., C.H., E.A.L., R.M., V.M., J.C.M., B.A.M., M.M., D.M.M., K.E.N., J.F.P., E.J.S., J.V., G.M.W., O.W., A.M.W., K.C.W., J.R.W., S.K.Y., Q.Z. Analysis preparation for manuscript: J.C.C., K.F., D.G., A.G., K.H.H., C.H., R.K., D.K., H.H.K., O.K., K.P.L., R.E.L., J.R., J.F.S., P.D.S., N.S. Data release: L.A., T.B., I.A.C., K.C., H.H.C., N.J.D., D.J.D., A.M.E., V.M.F., L.F., J.M.G., S.G., S.K.H., M.E.H., C.J., V.J., C.K., A.A.M., V.M.M., T.M., M.M., D.M.M., J.O., K.P., J.F.P., C.P., X.Q., R.K.S., N.S., I.S., E.J.S., D.V.W., O.W., K.W., K.C.W., C.Y., B.P.Y., Q.Z. Methods and research development: S.A., H.M.A., M.B., D.M.C., A.M.E., R.L.E., M.F., S.F., M.G.F., D.C.F., D.G., G.G., B.J.H., S.K.H., M.E.H., W.A.K., N.L., K.L., V.M., E.R.M., B.A.M., M.M., D.M.M., C.N., J.F.P., M.E.P., X.Q., M.C.R., C.R., E.J.S., S.M.S., D.G.T., D.V.W., G.M.W., Y.W., K.M.W., S.Y., B.P.Y., S.K.Y., Q.Z. DNA sequence production: S.A., E.A., T.A., T.B., C.J.B., D.A.B., K.D.D., S.P.D., A.M.E., R.L.E., C.N.F., S.F., C.C.F., L.L.F., R.S.F., B.H., S.K.H., M.E.H., V.J., C.L.K., S.L.L., N.L., L.L., D.M.M., I.N., C.N., M.O., J.F.P., X.Q., J.G.R., Y.R., M.C.R., D.V.W., Y.W., B.P.Y., Y.Z. Clinical sample collection: K.M.A., M.A.C., W.M.D., L.L.F., N.G., H.A.H., E.L.H., J.A.K., W.A.K., T.M., A.L.M., P.M., S.M.P., J.F.P., G.A.S., J.V., M.A.W., G.M.W. Body site experts: K.M.A., E.A.V., G.A., L.B., M.J.B., C.C.D., F.E.D., L.F., J.I., J.A.K., S.K.H., H.H.K., K.P.L., P.J.M., J. Ravel, T.M.S., J.A.S., J.D.S., J.V. Ethical, legal and social implications: R.M.F., D.E.H., W.A.K., N.B.K., C.M.L., A.L.M., R.R., P. Sankar, R.R.S., P. Spicer, L.Z. Strain management: E.A.V., J.H.B., I.A.C., K.C., S.W.C., H.H.C., T.Z.D., A.S.D., A.M.E., M.G.F., M.G.G., S.K.H., V.J., N.C.K., S.L.L., L.L., K.L., E.A.L., V.M.M., B.A.M., D.M.M., K.E.N., I.N., I.P., L.S., E.J.S., C.M.T., M.T., D.V.W., G.M.W., A.M.W., Y.W., K.M.W., B.P.Y., L.Z., Y.Z. 16S data analysis: K.M.A., E.J.A., G.L.A., C.A.A., M.B., B.W.B., J.P.B., G.A.B., S.R.C., S.C., J.C., T.Z.D., F.E.D., E.D., A.M.E., R.C.E., K.F., M.F., A.A.F., J.F., H.G., D.G., B.J.H., T.A.H., S.M.H., C.H., J.I., J.K.J., S.T.K., S.K.H., R.K., H.H.K., O.K., P.S.L., R.E.L., K.L., C.A.L., D.M., B.A.M., K.A.M., M.M., M.P., J.F.P., M.P., K.S.P., X.Q., J. Raes, K.P.R., M.C.R., B.R., J.F.S., P.D.S., T.M.S., N.S., J.A.S., W.D.S., T.J.S., C.S.S., E.J.S., R.M.T., J.V., T.A.V., Z.W., D.V.W., G.M.W., J.R.W., K.M.W., Y.Y., S.Y., Y.Z. Shotgun data processing and alignments: C.J.B., J.C.C., E.D., D.G., A.G., M.E.H., H.J., D.K., K.C.K., C.L.K., Y.L., J.C.M., B.A.M., M.M., D.M.M., J.O., J.F.P., X.Q., J.G.R., R.K.S., N.U.S., I.S., E.J.S., G.G.S., S.M.S., J.W., Z.W., G.M.W., O.W., K.C.W., T.W., S.K.Y., L.Z. Assembly: H.M.A., C.J.B., P.S.C., L.C., Y.D., S.P.D., M.G.F., M.E.H., H.J., S.K., B.L., Y.L., C.L., J.C.M., J.M.M., J.R.M., P.J.M., M.M., J.F.P., M.P., M.E.P., X.Q., M.R., R.K.S., M.S., D.D.S., G.G.S., S.M.S., C.M.T., T.J.T., W.W., G.M.W., K.C.W., L.Y., Y.Y., S.K.Y., L.Z. Annotation: O.O.A., V.B., C.J.B., I.A.C., A.T.C., K.C., H.H.C., A.S.D., M.G.G., J.M.G., J.G., A.G., S.G., B.J.H., K.H., S.K.H., C.H., H.J., N.C.K., R.M., V.M.M., K.M., T.M., M.M., J.O., K.P., M.P., X.Q., N.S., E.J.S., G.G.S., S.M.S., M.T., G.M.W., K.C.W., J.R.W., C.Y., S.K.Y., Q.Z., L.Z., W.G.S. Metabolic reconstruction: S.A., B.L.C., J.G., C.H., J.I., B.A.M., M.M., B.R., A.M.S., N.S., M.T., G.M.W., S.Y., Q.Z., J.D.Z.
相应的作者
道德声明
相互竞争的利益
作者声明没有竞争的经济利益。
额外的信息
在这项研究中使用的所有数据可用fromtheHuman微生物项目数据分析和协调中心http://hmpdacc.org并从NCBI。
权利和权限
本文根据分布Creative Commons Attribution-Non-Commercial-Share都许可证(http://creativecommons.org/licenses/by-nc-sa/3.0/)。
关于这篇文章
引用这篇文章
人类微生物组项目财团。结构、功能和人类健康的微生物多样性。自然486年,207 - 214 (2012)。https://doi.org/10.1038/nature11234
收到了:
接受:
发表:
发行日期:
DOI:https://doi.org/10.1038/nature11234
本文引用的
细菌的组成和群落结构在婴儿和儿童下呼吸道反复喘息:病例对照研究
意大利儿科杂志》(2022)
奴才,便携式读音序器,使快速阴道微生物群分析在临床设置
BMC医学基因组学(2022)
标准直肠拭子作为肠道微生物监控代理示例在重症监护
BMC微生物学(2022)
载人火星之旅及其对人类微生物组的影响
微生物组(2022)
玉米穗轴结构牙菌斑揭示小环境分类单元特异性
微生物组(2022)